Il DNA satellite gioca un ruolo chiave nella speciazione
I ricercatori mostrano come il DNA satellite organizza i cromosomi nelle cellule. Sospettano che questi segmenti di DNA, precedentemente ritenuti scarti genetici, siano uno dei motivi per cui specie diverse non possono incrociarsi con successo.
Oltre il 10% del nostro genoma è costituito da tratti di materiale genetico ripetitivi e apparentemente senza senso, noti come DNA satellite. Questo materiale non contiene nemmeno i progetti per le proteine. Alcuni scienziati l'hanno quindi etichettato come "spazzatura genetica".
In una serie di studi, Madhav Jagannathan, attualmente professore assistente presso il Dipartimento di biologia dell'ETH di Zurigo, e il suo ex supervisore post-dottorato Yukiko Yamashita del Whitehead Institute del MIT (USA) hanno dimostrato che il DNA satellite non è solo spazzatura, ma svolge un ruolo essenziale nelle cellule: collabora con le proteine della cellula per tenere insieme tutti i cromosomi di una cellula nel suo nucleo.
Nel loro ultimo lavoro, pubblicato di recente sulla rivista "Molecular Biology and Evolution", Jagannathan e Yamashita fanno un ulteriore passo avanti. Suggeriscono che il sistema di organizzazione dei cromosomi tramite il DNA satellite è un motivo importante per cui organismi di specie diverse non possono produrre prole vitale.
L'origine delle specie: l'uscita del DNA
? noto da anni che il DNA satellitare è altamente variabile tra le specie. "Se si confronta il genoma dello scimpanzé con quello dell'uomo, le regioni che codificano le proteine sono identiche al 98-99%", spiega Yamashita. "Ma il DNA spazzatura delle due specie è molto diverso".
Il DNA satellite è la sequenza del genoma che cambia più velocemente. "L'opinione attuale è che si tratti 'solo' di spazzatura genetica che non ha importanza se differisce da specie a specie", spiega il professore assistente presso il Dipartimento di biologia dell'ETH.
Tuttavia, quando lui e i suoi colleghi hanno studiato l'importanza del DNA satellite per la fertilità e la sopravvivenza delle specie "pure", hanno ricevuto la prima indicazione che queste sequenze potrebbero svolgere un ruolo nella speciazione.
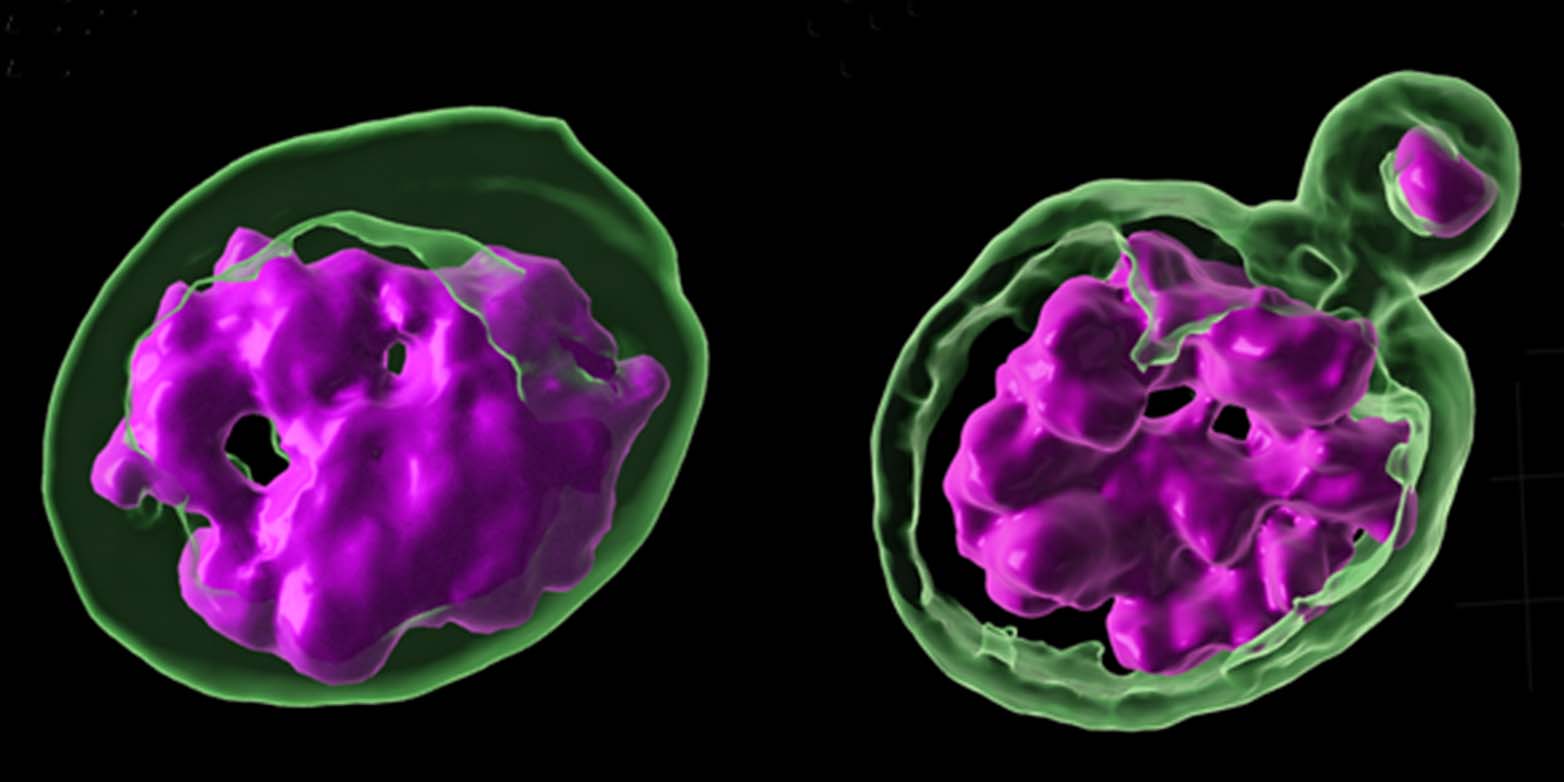
In uno dei loro esperimenti, i ricercatori hanno scambiato un moscerino della frutta con un altro moscerino. Drosophila melanogaster Una proteina chiamata "Prod". Di conseguenza, i cromosomi delle mosche si sono dispersi al di fuori del nucleo cellulare e si sono depositati in minuscoli ammassi di materiale cellulare. Le mosche sono morte. Normalmente, "Prod" si lega a un sito specifico sul DNA satellite di questo moscerino della frutta. "Questo pezzo di DNA satellitare, a cui si aggancia la proteina Prod, manca nei parenti più stretti di Drosophila melanogaster completa", afferma Jagannathan.
Se questo specifico pezzo di DNA satellite è essenziale per la sopravvivenza in una specie, ma manca nell'altra, ciò potrebbe significare che queste due specie di mosche hanno evoluto nel tempo sequenze di DNA satellite diverse per lo stesso compito: l'organizzazione dei cromosomi. Jagannathan e Yamashita si sono quindi chiesti se queste differenze evolutive potessero essere una ragione per cui specie diverse non possono riprodursi tra loro.
La storia di due specie di moscerini della frutta
Per studiare come le differenze nel DNA satellite influenzino l'incompatibilità riproduttiva, i ricercatori si sono concentrati su Drosophila melanogaster e i loro parenti più stretti, Drosophila simulans. Queste due specie si sono separate circa due milioni di anni fa.
Gli scienziati possono creare un Drosophila melanogaster-Femmina con a Drosophila simulans-I maschi si accoppiano, ma la prole è sterile o muore.
Jagannathan e Yamashita hanno quindi analizzato i tessuti di questi ibridi per scoprire cosa ne causasse la morte. I ricercatori si sono subito resi conto di una cosa interessante: Il tessuto degli ibridi mostrava esattamente le stesse caratteristiche del tessuto di mosche di specie "pure" con DNA satellitare danneggiato: in entrambe le forme, i cromosomi erano sparsi nelle cellule e non raggruppati nel nucleo.
Tuttavia, i ricercatori sono riusciti a creare una mosca ibrida sana alterando alcuni geni, noti come geni di incompatibilità ibrida, nelle mosche madri. Questi geni possono essere rilevati nel DNA satellite delle cellule delle specie pure e hanno influenzato l'impacchettamento dei cromosomi negli ibridi dell'esperimento.
Nel complesso, questi risultati indicano che le proteine che legano il DNA satellite devono cambiare con la stessa velocità del DNA satellite, che cambia rapidamente. Solo in questo modo le proteine di legame possono garantire la corretta organizzazione dei cromosomi nel nucleo della cellula. Nel corso del tempo, ogni specie sviluppa una propria "strategia" per gestire il DNA satellite. Se due specie affini con strategie diverse si incrociano, i cromosomi si disperdono al di fuori del nucleo cellulare.
Negli studi futuri, Jagannathan e Yamashita vogliono testare ulteriormente il loro modello: se riuscissero a progettare una proteina in grado di legare il DNA satellite di due specie diverse, potrebbero teoricamente ottenere un incrocio vitale in grado di produrre anche una prole. Tuttavia, per raggiungere questo obiettivo saranno necessari anni di ulteriori ricerche.
Questo testo di Eva Frederick del Whitehead Institute, MIT, è apparso per la prima volta supagina esternaqui.
Riferimento alla letteratura
Jagannathan M, Yamashita Y. Il difetto di raggruppamento del DNA satellite nei cromocentri è alla base dell'incompatibilità ibrida in Drosophila. Molecular Biology and Evolution, msab221. Pubblicato il 24 luglio 2021: pagina esterna10.1093/molbev/msab221